This is an old revision of the document!
Table of Contents
Gradient Descent
task: y hat = a + b*x 의 regression 에서 a 와 b를 구하기
- regressin line으로 이루어지는 에측치로 결과되는 오차의 제곱의 합은 최소값이 되어야 한다.
- 방법 1. (안되는 방법)
- 우선 b를 안다고 하고 정해두면 (가령 -2.4와 같이 – 비현실적이지만)
- 예측할 수 있는 a값의 range를 두고
- 하나씩 대입하여 그 때의 sum of square residual 을 (ssr 혹은 sse) 구해서
- 기록해 두면서 어디서 최소값인지 본다.
- 아래 r script는 이런 방법으로 구해 본것인데 아래처럼 두가지 단점이 있다.
- 우선 정확한 b값을 알 수는 없다.
- a 값을 장님 문고리 잡듯이 -50에서 50 사이의 점수를 0.1씩 증가시켜 보는 것이 너무 비효율적이다.
- 더불어 이렇게 구한 a값은 1/10 단위의 숫자를 구하게 되지 정확한 a값을 구하는 것은 아니다 (예를 들면 1.4로 a값을 구했는데 정확한 값은 1.38976 일 수도 있다.
rs01
library(tidyverse)
library(data.table)
library(ggplot2)
library(ggpmisc)
rm(list=ls())
# set.seed(191)
nx <- 200
mx <- 4.5
sdx <- mx * 0.56
x <- rnorm(nx, mx, sdx)
slp <- 12
y <- slp * x + rnorm(nx, 0, slp*sdx*3)
data <- data.frame(x, y)
mo <- lm(y ~ x, data = data)
summary(mo)
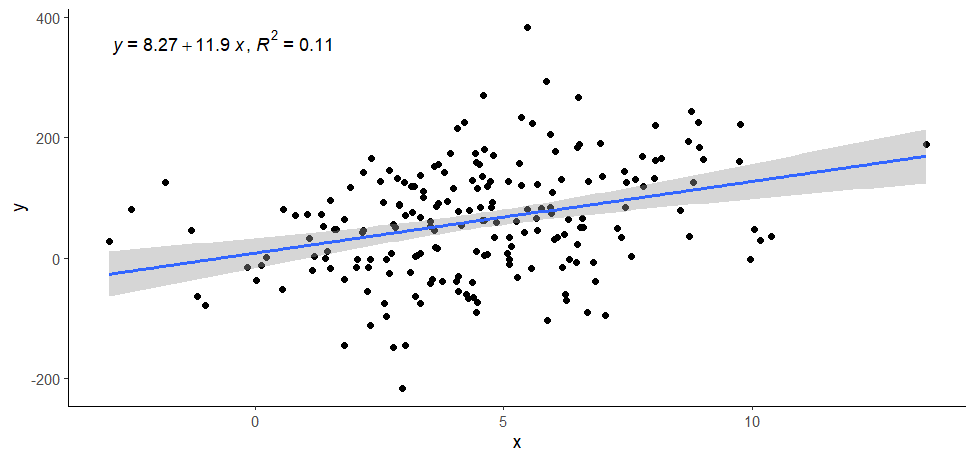
ggplot(data = data, aes(x = x, y = y)) +
geom_point() +
stat_poly_line() +
stat_poly_eq(use_label(c("eq", "R2"))) +
theme_classic()
# set.seed(191)
# Initialize random betas
# 우선 b를 고정하고 a만
# 변화시켜서 이해
b <- summary(mo)$coefficients[2]
a <- 0
b.init <- b
a.init <- a
# Predict function:
predict <- function(x, a, b){
return (a + b * x)
}
# And loss function is:
residuals <- function(predictions, y) {
return(y - predictions)
}
# we use sum of square of error which oftentimes become big
ssrloss <- function(predictions, y) {
residuals <- (y - predictions)
return(sum(residuals^2))
}
ssrs <- c() # for sum of square residuals
srs <- c() # sum of residuals
as <- c() # for as (intercepts)
for (i in seq(from = -50, to = 50, by = 0.01)) {
pred <- predict(x, i, b)
res <- residuals(pred, y)
ssr <- ssrloss(pred, y)
ssrs <- append(ssrs, ssr)
srs <- append(srs, sum(res))
as <- append(as, i)
}
length(ssrs)
length(srs)
length(as)
min(ssrs)
min.pos.ssrs <- which(ssrs == min(ssrs))
min.pos.ssrs
print(as[min.pos.ssrs])
summary(mo)
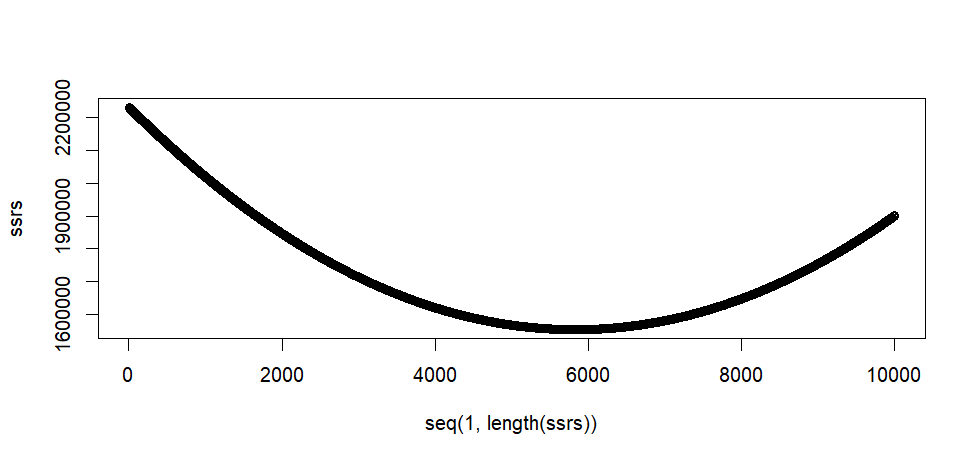
plot(seq(1, length(ssrs)), ssrs)
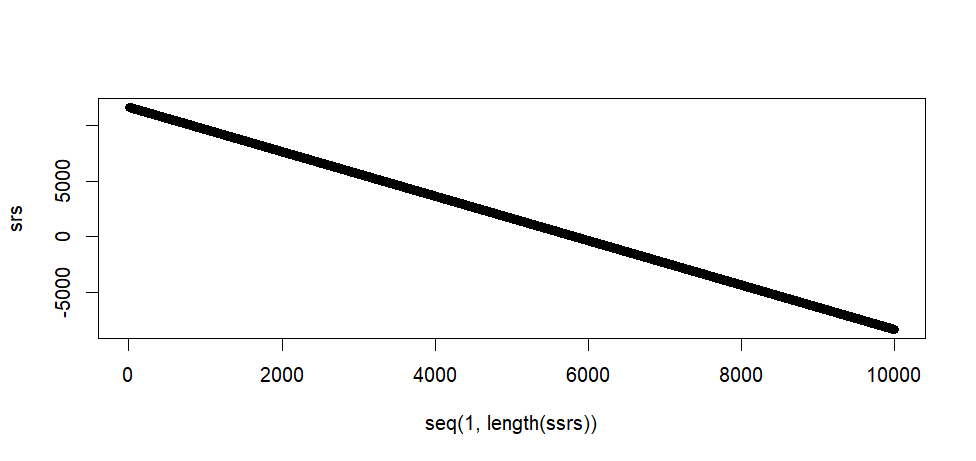
plot(seq(1, length(ssrs)), srs)
tail(ssrs)
max(ssrs)
min(ssrs)
tail(srs)
max(srs)
min(srs)
ro01
> library(ggplot2)
> library(ggpmisc)
>
> rm(list=ls())
> # set.seed(191)
> nx <- 200
> mx <- 4.5
> sdx <- mx * 0.56
> x <- rnorm(nx, mx, sdx)
> slp <- 12
> y <- slp * x + rnorm(nx, 0, slp*sdx*3)
>
> data <- data.frame(x, y)
>
> mo <- lm(y ~ x, data = data)
> summary(mo)
Call:
lm(formula = y ~ x, data = data)
Residuals:
Min 1Q Median 3Q Max
-259.314 -59.215 6.683 58.834 309.833
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) 8.266 12.546 0.659 0.511
x 11.888 2.433 4.887 2.11e-06 ***
---
Signif. codes: 0 ‘***’ 0.001 ‘**’ 0.01 ‘*’ 0.05 ‘.’ 0.1 ‘ ’ 1
Residual standard error: 88.57 on 198 degrees of freedom
Multiple R-squared: 0.1076, Adjusted R-squared: 0.1031
F-statistic: 23.88 on 1 and 198 DF, p-value: 2.111e-06
>
> ggplot(data = data, aes(x = x, y = y)) +
+ geom_point() +
+ stat_poly_line() +
+ stat_poly_eq(use_label(c("eq", "R2"))) +
+ theme_classic()
> # set.seed(191)
> # Initialize random betas
> # 우선 b를 고정하고 a만
> # 변화시켜서 이해
> b <- summary(mo)$coefficients[2]
> a <- 0
>
> b.init <- b
> a.init <- a
>
> # Predict function:
> predict <- function(x, a, b){
+ return (a + b * x)
+ }
>
> # And loss function is:
> residuals <- function(predictions, y) {
+ return(y - predictions)
+ }
>
> # we use sum of square of error which oftentimes become big
> ssrloss <- function(predictions, y) {
+ residuals <- (y - predictions)
+ return(sum(residuals^2))
+ }
>
> ssrs <- c() # for sum of square residuals
> srs <- c() # sum of residuals
> as <- c() # for as (intercepts)
>
> for (i in seq(from = -50, to = 50, by = 0.01)) {
+ pred <- predict(x, i, b)
+ res <- residuals(pred, y)
+ ssr <- ssrloss(pred, y)
+ ssrs <- append(ssrs, ssr)
+ srs <- append(srs, sum(res))
+ as <- append(as, i)
+ }
> length(ssrs)
[1] 10001
> length(srs)
[1] 10001
> length(as)
[1] 10001
>
> min(ssrs)
[1] 1553336
> min.pos.ssrs <- which(ssrs == min(ssrs))
> min.pos.ssrs
[1] 5828
> print(as[min.pos.ssrs])
[1] 8.27
> summary(mo)
Call:
lm(formula = y ~ x, data = data)
Residuals:
Min 1Q Median 3Q Max
-259.314 -59.215 6.683 58.834 309.833
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) 8.266 12.546 0.659 0.511
x 11.888 2.433 4.887 2.11e-06 ***
---
Signif. codes: 0 ‘***’ 0.001 ‘**’ 0.01 ‘*’ 0.05 ‘.’ 0.1 ‘ ’ 1
Residual standard error: 88.57 on 198 degrees of freedom
Multiple R-squared: 0.1076, Adjusted R-squared: 0.1031
F-statistic: 23.88 on 1 and 198 DF, p-value: 2.111e-06
> plot(seq(1, length(ssrs)), ssrs)
> plot(seq(1, length(ssrs)), srs)
> tail(ssrs)
[1] 1900842 1901008 1901175 1901342 1901509 1901676
> max(ssrs)
[1] 2232329
> min(ssrs)
[1] 1553336
> tail(srs)
[1] -8336.735 -8338.735 -8340.735 -8342.735 -8344.735 -8346.735
> max(srs)
[1] 11653.26
> min(srs)
[1] -8346.735
>
>
위 방법은 dumb . . . . .
우선 a의 범위가 어디가 될지 몰라서 -50 에서 50까지로 한것
이 두 지점 사이를 0.01 단위로 증가시킨 값을 a값이라고 할 때의 sse값을 구하여 저장한 것
이렇게 구한 sse 값들 중 최소값일 때의 a값을 regression의 a값으로 추정한 것.
이렇게 해서 구한 값은 summary(mo)에서의 a와 값과 같다.
SSE 대신에 MSE를 쓰기
#####
# with mean square error (mse) instead of sse
b <- summary(mo)$coefficients[2]
a <- 0
# we use sum of square of error which oftentimes become big
msrloss <- function(predictions, y) {
residuals <- (y - predictions)
return(mean(residuals^2))
}
msrs <- c() # for sum of square residuals
srs <- c() # sum of residuals
as <- c() # for as (intercepts)
for (i in seq(from = -50, to = 50, by = 0.01)) {
pred <- predict(x, i, b)
res <- residuals(pred, y)
msr <- msrloss(pred, y)
msrs <- append(msrs, msr)
srs <- append(srs, mean(res))
as <- append(as, i)
}
length(msrs)
length(srs)
length(as)
min(msrs)
min.pos.msrs <- which(msrs == min(msrs))
min.pos.msrs
print(as[min.pos.msrs])
summary(mo)
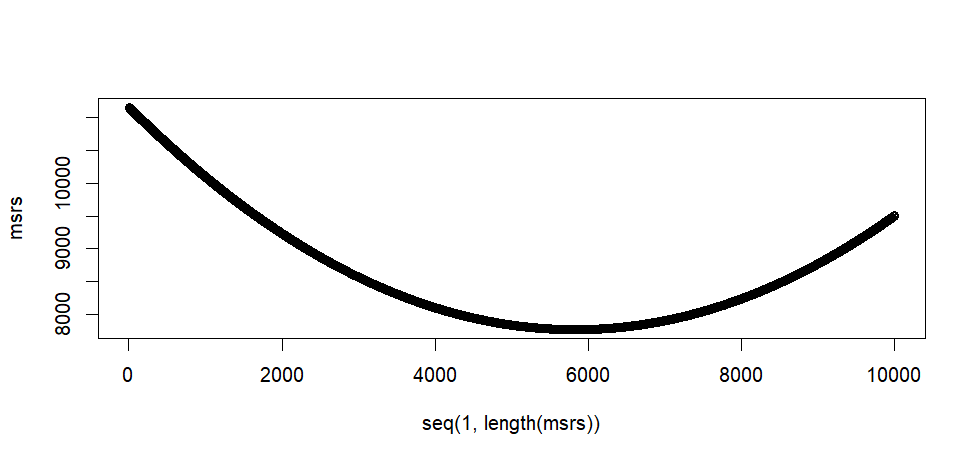
plot(seq(1, length(msrs)), msrs)
plot(seq(1, length(srs)), srs)
tail(msrs)
max(msrs)
min(msrs)
tail(srs)
max(srs)
min(srs)
output
> #####
> # with mean square error (mse) instead of sse
>
> b <- summary(mo)$coefficients[2]
> a <- 0
>
> # we use sum of square of error which oftentimes become big
> msrloss <- function(predictions, y) {
+ residuals <- (y - predictions)
+ return(mean(residuals^2))
+ }
>
> msrs <- c() # for sum of square residuals
> srs <- c() # sum of residuals
> as <- c() # for as (intercepts)
>
> for (i in seq(from = -50, to = 50, by = 0.01)) {
+ pred <- predict(x, i, b)
+ res <- residuals(pred, y)
+ msr <- msrloss(pred, y)
+ msrs <- append(msrs, msr)
+ srs <- append(srs, mean(res))
+ as <- append(as, i)
+ }
> length(msrs)
[1] 10001
> length(srs)
[1] 10001
> length(as)
[1] 10001
>
> min(msrs)
[1] 7766.679
> min.pos.msrs <- which(msrs == min(msrs))
> min.pos.msrs
[1] 5828
> print(as[min.pos.msrs])
[1] 8.27
> summary(mo)
Call:
lm(formula = y ~ x, data = data)
Residuals:
Min 1Q Median 3Q Max
-259.314 -59.215 6.683 58.834 309.833
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) 8.266 12.546 0.659 0.511
x 11.888 2.433 4.887 2.11e-06 ***
---
Signif. codes: 0 ‘***’ 0.001 ‘**’ 0.01 ‘*’ 0.05 ‘.’ 0.1 ‘ ’ 1
Residual standard error: 88.57 on 198 degrees of freedom
Multiple R-squared: 0.1076, Adjusted R-squared: 0.1031
F-statistic: 23.88 on 1 and 198 DF, p-value: 2.111e-06
> plot(seq(1, length(msrs)), msrs)
> plot(seq(1, length(srs)), srs)
> tail(msrs)
[1] 9504.208 9505.041 9505.875 9506.710 9507.544 9508.379
> max(msrs)
[1] 11161.64
> min(msrs)
[1] 7766.679
> tail(srs)
[1] -41.68368 -41.69368 -41.70368 -41.71368 -41.72368 -41.73368
> max(srs)
[1] 58.26632
> min(srs)
[1] -41.73368
>
b값 구하기
이제는 a값을 고정하고 b값도 같은 방식으로 구해볼 수 있다
rs01
##############################################
# b값도 범위를 추측한 후에 0.01씩 증가시키면서
# 각 b값에서 mse값을 구해본후 가장 작은 값을
# 가질 때의 b값을 구하면 된다.
# 그러나 b값의 적절한 구간을 예측하는 것이
# 불가능하다 (그냥 추측뿐)
# 위의 y 데이터에서 y = 314*x + rnorm(. . .)
# 이라면 -30-30 구간은 적절하지 않은 구간이 된다.
# 더우기 a값을 정확히 알아야 b값을 추출할 수 있다.
# 이는 적절한 방법이 아니다.
b <- 1
a <- summary(mo)$coefficients[1]
b.init <- b
a.init <- a
# Predict function:
predict <- function(x, a, b){
return (a + b * x)
}
# And loss function is:
residuals <- function(predictions, y) {
return(y - predictions)
}
# we use sum of square of error which oftentimes become big
msrloss <- function(predictions, y) {
residuals <- (y - predictions)
return(mean(residuals^2))
}
msrs <- c()
mrs <- c()
as <- c()
for (i in seq(from = -50, to = 50, by = 0.01)) {
pred <- predict(x, a, i)
res <- residuals(pred, y)
msr <- msrloss(pred, y)
msrs <- append(msrs, msr)
mrs <- append(mrs, mean(res))
as <- append(as,i)
}
min(msrs)
min.pos.msrs <- which(msrs == min(msrs))
print(as[min.pos.msrs])
summary(mo)
plot(seq(1, length(msrs)), msrs)
plot(seq(1, length(mrs)), mrs)
min(msrs)
max(msrs)
min(mrs)
max(mrs)
ro01
>
> ##############################################
> # b값도 범위를 추측한 후에 0.01씩 증가시키면서
> # 각 b값에서 mse값을 구해본후 가장 작은 값을
> # 가질 때의 b값을 구하면 된다.
> # 그러나 b값의 적절한 구간을 예측하는 것이
> # 불가능하다 (그냥 추측뿐)
> # 위의 y 데이터에서 y = 314*x + rnorm(. . .)
> # 이라면 -30-30 구간은 적절하지 않은 구간이 된다.
> # 더우기 a값을 정확히 알아야 b값을 추출할 수 있다.
> # 이는 적절한 방법이 아니다.
>
> b <- 1
> a <- summary(mo)$coefficients[1]
>
> b.init <- b
> a.init <- a
>
> # Predict function:
> predict <- function(x, a, b){
+ return (a + b * x)
+ }
>
> # And loss function is:
> residuals <- function(predictions, y) {
+ return(y - predictions)
+ }
>
> # we use sum of square of error which oftentimes become big
> msrloss <- function(predictions, y) {
+ residuals <- (y - predictions)
+ return(mean(residuals^2))
+ }
>
> msrs <- c()
> mrs <- c()
> as <- c()
>
> for (i in seq(from = -50, to = 50, by = 0.01)) {
+ pred <- predict(x, a, i)
+ res <- residuals(pred, y)
+ msr <- msrloss(pred, y)
+ msrs <- append(msrs, msr)
+ mrs <- append(mrs, mean(res))
+ as <- append(as,i)
+ }
>
> min(msrs)
[1] 7766.679
> min.pos.msrs <- which(msrs == min(msrs))
> print(as[min.pos.msrs])
[1] 11.89
> summary(mo)
Call:
lm(formula = y ~ x, data = data)
Residuals:
Min 1Q Median 3Q Max
-259.314 -59.215 6.683 58.834 309.833
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) 8.266 12.546 0.659 0.511
x 11.888 2.433 4.887 2.11e-06 ***
---
Signif. codes: 0 ‘***’ 0.001 ‘**’ 0.01 ‘*’ 0.05 ‘.’ 0.1 ‘ ’ 1
Residual standard error: 88.57 on 198 degrees of freedom
Multiple R-squared: 0.1076, Adjusted R-squared: 0.1031
F-statistic: 23.88 on 1 and 198 DF, p-value: 2.111e-06
> plot(seq(1, length(msrs)), msrs)
> plot(seq(1, length(mrs)), mrs)
> min(msrs)
[1] 7766.679
> max(msrs)
[1] 109640
> min(mrs)
[1] -170.3106
> max(mrs)
[1] 276.56
>
a와 b를 동시에 구할 수 있는 방법은 없을까? 위의 방법으로는 어렵다. 일반적으로 우리는 a와 b값이 무엇이되는가를 미분을 이용해서 구할 수 있었다. R에서 미분의 해를 구하기 보다는 해에 접근하도록 하는 프로그래밍을 써서 a와 b의 근사값을 구한다. 이것을 gradient descent라고 부른다.
Gradient descend
위에서 a값이 무엇일 때 mse값이 최소가 될까를 봐서 이 때의 a값을 실제 $y = a + bx$ 의 a 값으로 삼았다. 이 때 a값의 추정을 위해서
seq(-10, 10, 0.01) 의 범위와 증가값을 가지고 일일이 대입하여 mse를 구아였다.
위에서의 0.01씩 증가시켜 대입하는 것이 아니라 처음 한 숫자에서 시작한 후 그 다음 숫자를 정한 후에 점진적으로 그 숫자 간격을 줄여가면서 보면 정율적으로 0.01씩 증가시키는 것 보다 효율적일 것 같다. 이 증가분을 구하기 위해서 미분을 사용한다.
점차하강 = 조금씩 깍아서 원하는 기울기 (미분값) 찾기
prerequisite:
표준편차 추론에서 평균을 사용하는 이유: 실험적_수학적_이해
deriviation of a and b in a simple regression
위의 문서는 a, b에 대한 값을 미분법을 이용해서 직접 구하였다. 컴퓨터로는 이렇게 하기가 쉽지 않다. 그렇다면 이 값을 반복계산을 이용해서 추출하는 방법은 없을까? gradient descent
\begin{eqnarray*}
\text{for a (constant)} \\
\\
\text{SSE} & = & \text{Sum of Square Residuals} \\
\text{Residual} & = & (Y_i - (a + bX_i)) \\
\\
\frac{\text{dSSE}}{\text{da}}
& = & \frac{\text{dResidual^2}}{\text{dResidual}} * \frac{\text{dResidual}}{\text{da}} \\
& = & 2 * \text{Residual} * \dfrac{\text{d}}{\text{da}} (Y_i - (a+bX_i)) \\
& \because & \dfrac{\text{d}}{\text{da}} (Y_i - (a+bX_i)) = -1 \\
& = & 2 * \sum{(Y_i - (a + bX_i))} * -1 \\
& = & -2 *\sum{\text{residual}} \\
& .. & -2 \frac{\sum{\text{residual}}}{n} \\
& = & -2 * \overline{\text{residual}} \\
\end{eqnarray*}
아래 R code에서 gradient function을 참조.
\begin{eqnarray*} \text{for b, (coefficient)} \\ \\ \dfrac{\text{d}}{\text{db}} \sum{(Y_i - (a + bX_i))^2} & = & \sum{\dfrac{\text{dResidual}^2}{\text{db}}} \\ & = & \sum{\dfrac{\text{dResidual}^2}{\text{dResidual}}*\dfrac{\text{dResidual}}{\text{db}} } \\ & = & \sum{2*\text{Residual} * \dfrac{\text{dResidual}}{\text{db}} } \\ & = & \sum{2*\text{Residual} * (-X_i) } \;\;\;\; \\ & \because & \dfrac{\text{dResidual}}{\text{db}} = (Y_i - (a+bX_i)) = -X_i \\ & = & -2 X_i \sum{(Y_i - (a + bX_i))} \\ & = & -2 * X_i * \sum{\text{residual}} \\ & .. & -2 * X_i * \frac{\sum{\text{residual}}}{n} \\ & = & -2 * \overline{X_i * \text{residual}} \\ \end{eqnarray*}
위의 설명은 Sum of Square값을 미분하는 것을 전제로 하였지만, Mean Square 값을 (Sum of Square값을 N으로 나눈 것) 대용해서 이해할 수도 있다. 아래의 code는 (미분을 이해한다는 것을 전제로) b값과 a값이 변할 때 msr (mean square residual) 값이 어떻게 변하는가를 알려주는 것이다.
gradient <- function(x, y, predictions){
error = y - predictions
db = -2 * mean(x * error)
da = -2 * mean(error)
return(list("b" = db, "a" = da))
}
위 펑션으로 얻은 da와 db값을 초기에 설정한 a, b 값에 더해 준 값을 다시 a, b값으로 하여 gradient 펑션을 통해서 다시 db, da값을 구하고 이를 다시 이전 단계에서 구한 a, b값에 더하여 그 값을 다시 a, b값을 하여 . . . .
위를 반복한다. 단, db값과 da값을 그냥 대입하기 보다는 초기에 설정한 learning.rate값을 (0.01 예를 들면) 곱하여 구한 값을 더하게 된다. 이것이 아래의 code이다.
gradient <- function(x, y, predictions){
error = y - predictions
db = -2 * mean(x * error)
da = -2 * mean(error)
return(list("b" = db, "a" = da))
}
mseloss <- function(predictions, y) {
residuals <- (y - predictions)
return(mean(residuals^2))
}
# Train the model with scaled features
learning_rate = 1e-2
lr = 1e-1
# Record Loss for each epoch:
logs = list()
as = c()
bs = c()
mse = c()
sse = c()
x.ori <- x
zx <- (x-mean(x))/sd(x)
nlen <- 50
for (epoch in 1:nlen) {
predictions <- predict(zx, a, b)
loss <- mseloss(predictions, y)
mse <- append(mse, loss)
grad <- gradient(zx, y, predictions)
step.b <- grad$b * lr
step.a <- grad$a * lr
b <- b-step.b
a <- a-step.a
as <- append(as, a)
bs <- append(bs, b)
}
a 와 b 값을 gradient descent 방법을 이용하여 한꺼번에 구하기
<tabbox rs01>
# the above no gradient
# mse 값으로 계산 rather than sse
# 후자는 값이 너무 커짐
a <- rnorm(1)
b <- rnorm(1)
a.start <- a
b.start <- b
gradient <- function(x, y, predictions){
error = y - predictions
db = -2 * mean(x * error)
da = -2 * mean(error)
return(list("b" = db, "a" = da))
}
mseloss <- function(predictions, y) {
residuals <- (y - predictions)
return(mean(residuals^2))
}
# Train the model with scaled features
learning.rate = 1e-1
# Record Loss for each epoch:
as = c()
bs = c()
mses = c()
sses = c()
mres = c()
zx <- (x-mean(x))/sd(x)
nlen <- 50
for (epoch in 1:nlen) {
predictions <- predict(zx, a, b)
residual <- residuals(predictions, y)
loss <- mseloss(predictions, y)
mres <- append(mres, mean(residual))
mses <- append(mses, loss)
grad <- gradient(zx, y, predictions)
step.b <- grad$b * learning.rate
step.a <- grad$a * learning.rate
b <- b-step.b
a <- a-step.a
as <- append(as, a)
bs <- append(bs, b)
}
mses
mres
as
bs
# scaled
a
b
# unscale coefficients to make them comprehensible
# see http://commres.net/wiki/gradient_descent#why_normalize_scale_or_make_z-score_xi
# and
# http://commres.net/wiki/gradient_descent#how_to_unnormalize_unscale_a_and_b
#
a = a - (mean(x) / sd(x)) * b
b = b / sd(x)
a
b
# changes of estimators
as <- as - (mean(x) /sd(x)) * bs
bs <- bs / sd(x)
as
bs
mres
mse.x <- mses
parameters <- data.frame(as, bs, mres, mses)
cat(paste0("Intercept: ", a, "\n", "Slope: ", b, "\n"))
summary(lm(y~x))$coefficients
mses <- data.frame(mses)
mses.log <- data.table(epoch = 1:nlen, mses)
ggplot(mses.log, aes(epoch, mses)) +
geom_line(color="blue") +
theme_classic()
# mres <- data.frame(mres)
mres.log <- data.table(epoch = 1:nlen, mres)
ggplot(mres.log, aes(epoch, mres)) +
geom_line(color="red") +
theme_classic()
ch <- data.frame(mres, mses)
ch
max(y)
ggplot(data, aes(x = x, y = y)) +
geom_point(size = 2) +
geom_abline(aes(intercept = as, slope = bs),
data = parameters, linewidth = 0.5,
color = 'green') +
stat_poly_line() +
stat_poly_eq(use_label(c("eq", "R2"))) +
theme_classic() +
geom_abline(aes(intercept = as, slope = bs),
data = parameters %>% slice_head(),
linewidth = 1, color = 'blue') +
geom_abline(aes(intercept = as, slope = bs),
data = parameters %>% slice_tail(),
linewidth = 1, color = 'red') +
labs(title = 'Gradient descent. blue: start, red: end, green: gradients')
summary(lm(y~x))
a.start
b.start
a
b
<tabbox ro01>
</tablox>
Why normalize (scale or make z-score) xi
x 변인의 측정단위로 인해서 b 값이 결정되게 되는데 이 때의 b값은 상당하고 다양한 범위를 가질 수 있다. 가령 월 수입이 (인컴) X 라고 한다면 우리가 추정해야 (추적해야) 할 b값은 수백만이 될 수도 있다.이 값을 gradient로 추적하게 된다면 너무도 많은 iteration을 거쳐야 할 수 있다. 변인이 바뀌면 이 b의 추적범위도 드라마틱하게 바뀌게 된다. 이를 표준화한 x 점수를 사용하게 된다면 일정한 learning rate와 iteration만으로도 정확한 a와 b를 추적할 수 있게 된다.
How to unnormalize (unscale) a and b
\begin{eqnarray*} y & = & a + b * x \\ & & \text{we use z instead of x} \\ & & \text{and } \\ & & z = \frac{(x - \mu)}{\sigma} \\ & & \text{suppose that the result after calculation be } \\ y & = & k + m * z \\ & = & k + m * \frac{(x - \mu)}{\sigma} \\ & = & k + \frac{m * x}{\sigma} - \frac{m * \mu}{\sigma} \\ & = & k - \frac{m * \mu}{\sigma} + \frac{m * x}{\sigma} \\ & = & \underbrace{k - \frac{\mu}{\sigma} * m}_\text{ 1 } + \underbrace{\frac{m}{\sigma}}_\text{ 2 } * x \\ & & \text{therefore, a and be that we try to get are } \\ a & = & k - \frac{\mu}{\sigma} * m \\ b & = & \frac{m}{\sigma} \\ \end{eqnarray*}
- gradient_descent:code01 - Page not found.
- gradient_descent:code02 - Page not found.
- gradient_descent:output01 - Page not found.
- gradient_descent:output02 - Page not found.